全基因组关联分析是复杂数量性状定位的有效手段,该分析不需要构建家系群体,使用自然群体即可同时对多个性状进行分析,找到与性状关联的SNP位点,进而找到与性状关联的候选区间。
那么,通过GWAS分析得到了与目标性状关联的SNPs位点/候选区间/候选基因,接下来该如何对这些结果进行验证呢?下面小编就为大家介绍几种方法,相信总有一种适合你。
01、GWAS+QTL定位结果验证
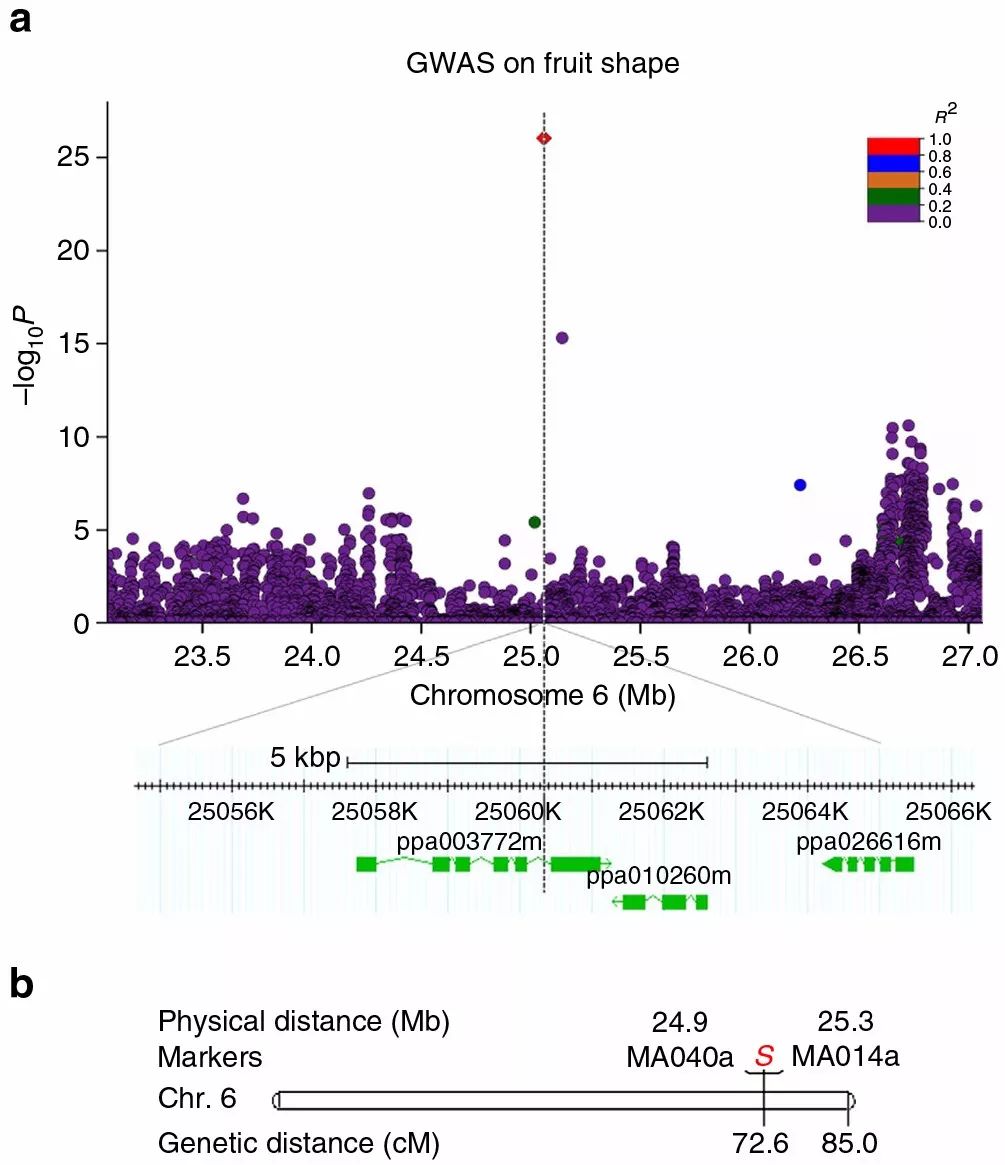
GWAS分析完成后,可以将分析结果与基于连锁分析得到QTL定位结果进行比较,验证GWAS分析结果的可靠性。一般而言,很多物种在GWAS分析之前,可能都会有相关的QTL定位结果,这为GWAS的验证提供了很好的资源。在桃子的GWAS分析文章中,作者对桃子果型进行GWAS分析,发现关联信号位于scaffold_6 (25,060,196 bp),这与之前分析得到的一个桃果型QTL一致,从而为GWAS结果的可靠性提供了依据。
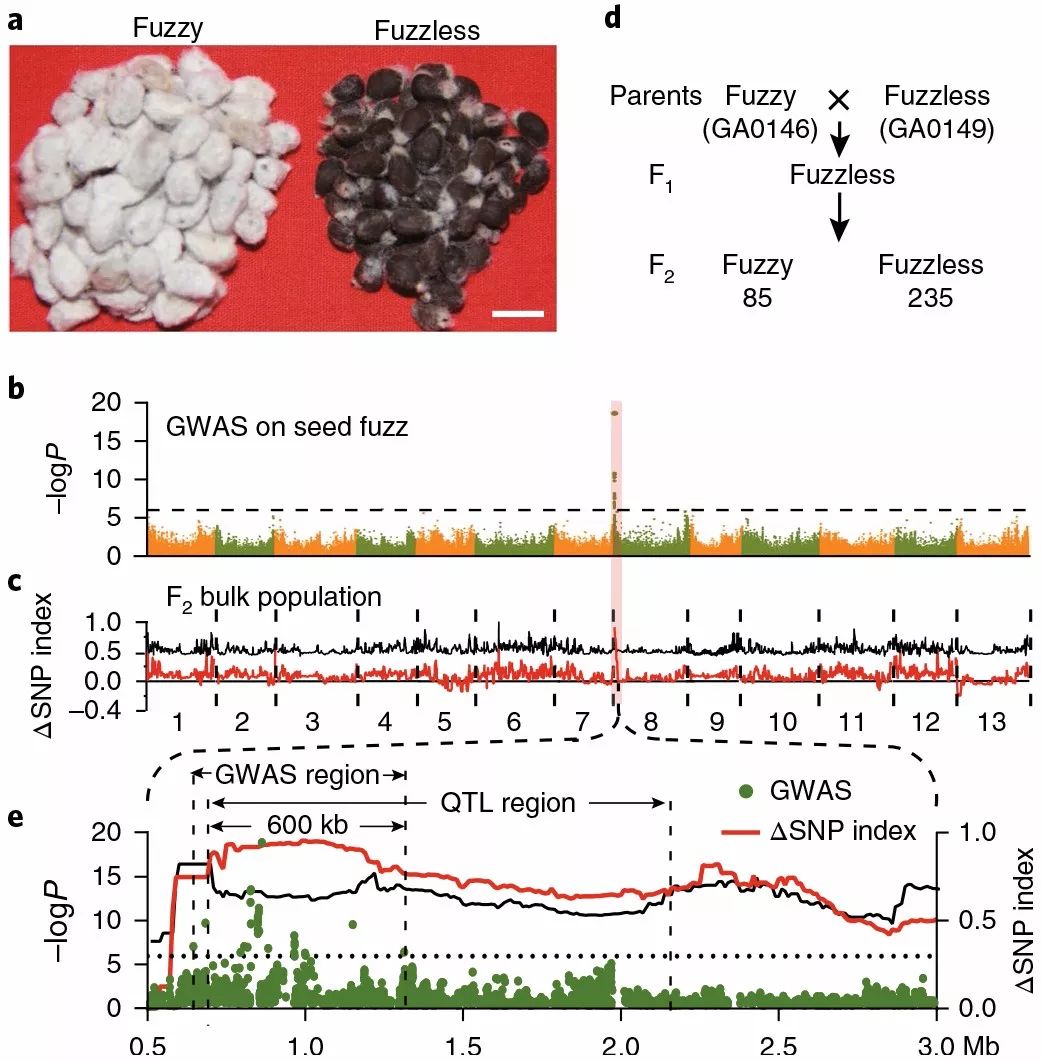
另外也可以通过GWAS分析结果与QTL-seq的分析结果进行比较,在对亚洲棉的棉绒相关基因的GWAS分析中,在8号染色体的~0.6 to ~1.3 Mb区间发现了强的关联信号;然后作者又进行了QTL-seq的实验,发现QTL区间是位于8号染色体的~0.70 to ~2.15 Mb区间,两者的结果相互验证,进一步说明了分析结果的可靠性。
02、GWAS+qRT-PCR验证
(文章:Genomic analyses in cotton identify signatures of selection and loci associated with fiber quality and yield traits)
通过GWAS分析得到了候选的功能基因后,从研究的材料中选取性状有差异的个体,对候选基因进行qRT-PCR分析,通过基因表达量的差异进行验证。该分析方法简单快速,是分析中常用的验证方法。
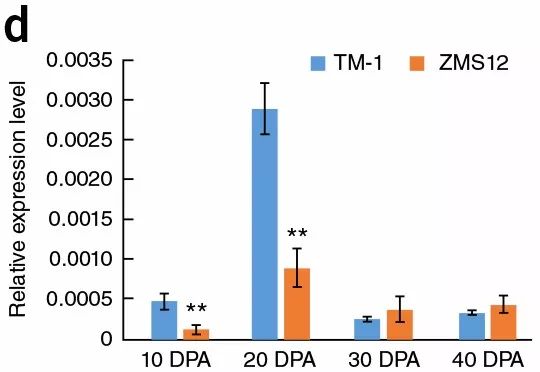
2017年发表在NG上的棉花群体进化+全基因组关联分析的文章中,作者通过GWAS分析鉴定了一个与棉花衣分有关的候选基因AIL6,然后挑选了低棉花衣分的TM-1植株与高棉花衣分的ZMS12植株,通过qRT-PCR分析了该基因在不同样本的表达量,发现TM-1中在胚珠发育的10-20天该基因的表达量比ZMS12中高约10倍。
03、GWAS+基因过表达验证
(文章:Genome-wide association study using whole-genome sequencing rapidly identifies new genes influencing agronomic traits in rice)
通过GWAS得到候选功能基因后,也可以通过转基因进行基因过表达的方式对基因的功能进行验证。水稻的关联分析中作者发现基因LOC_Os01g62780对水稻的抽穗时间有影响,于是将含有单倍型A和B的基因序列引入到含有单倍型A的日本晴中。结果表明转入单倍型A的植物表型没有发生改变,而转入单倍型B的植物抽穗期变晚。从而证明LOC_Os01g62780基因是控制水稻抽穗时间的基因。
04、GWAS+基因沉默验证
(陆地棉文章:Resequencing a core collection of upland cotton identifies genomic variation and loci influencing fiber quality and yield)
通过病毒诱导的基因沉默的方法对GWAS分析得到的基因进行功能验证。在棉花的GWAS分析中,鉴定到了一个与早期开花有关的基因GhCIP1。采用VIGS(病毒诱导的基因沉默)对基因GhCIP1功能进行验证,发现处理组植株没有形成花枝,对照组(non-VIGS)植株在同一生长条件下能产生3个花枝,进一步表明基因GhCIP1能够影响棉花的早期开花。
以上是GWAS分析结果验证的相关方法,看了这些介绍,您是否已经知道您的下一步研究方向了(悄悄告诉你哈,做了这些相关验证,真的是可能发NG级别的文章的)?如果您有GWAS相关的研究,请联系我们,一起开启您的研究之旅,当然啦,顺带着也可以收获篇高水平文章啦!
参考文献
1.Cao K , Zhou Z , Wang Q , et al. Genome-wide association study of 12 agronomic traits in peach[J]. Nature Communications, 2016.
2.Du XM, Huang G, et al. Resequencing of 243 diploid cotton accessions based on an updated A genome identifies the genetic basis of key agronomic traits [J] . Nature Genetics, 2018.
3.Fang L, Wang Q, et al. Genomic analyses in cotton identify signatures of selection and loci associated with fiber quality and yield traits [J]. Nature Genetics, 2017
4.Yano K , Yamamoto E , Aya K , et al. Genome-wide association study using whole-genome sequencing rapidly identifies new genes influencing agronomic traits in rice[J]. Nature Genetics, 2016.
5.Ma Zhy, He Shp, et al. Resequencing a core collection of upland cotton identifies genomic variation and loci influencing fiber quality and yield [J]. Nature Genetics, 2018